导读
信使RNA(mRNA)的5'非翻译区(5' UTR)在调控蛋白质合成的起始阶段扮演着核心角色。该区域包含多种顺式调控元件,其中Kozak序列和上游开放阅读框(uORF)尤为关键。
Kozak序列的强度直接影响核糖体对主编码序列(CDS)起始密码子的识别效率。uORF则通过翻译自身,可能导致下游CDS的翻译效率降低(因核糖体解离)或继续进行。
这些5' UTR元件内的遗传变异,例如改变Kozak序列强度或创建、破坏uORF,能够显著影响翻译效率,进而改变蛋白质产量。尽管已有研究表明这类变异可导致人类疾病,但由于其调控机制复杂且多样,系统性地识别和评估其功能影响仍然是一个巨大的挑战。
2026年4月2日,洛克菲勒大学Peng Zhang与Aurélie Cobat团队合作,在American Journal of Human Genetics上发表了题为“Genome-wide detection of human 5' UTR variants that impact protein translation”的论文。该研究开发了一种名为5ULTRA的计算方法,它通过整合17个生物学特征来系统性地检测和优先排序影响蛋白质翻译的5' UTR变异。

文章索引
【标题】Genome-wide detection of human 5' UTR variants that impact protein translation
【发表期刊】American Journal of Human Genetics
【发表日期】2026年4月2日
【作者及团队】洛克菲勒大学Peng Zhang和Aurélie Cobat团队
【IF】8.1
研究结果
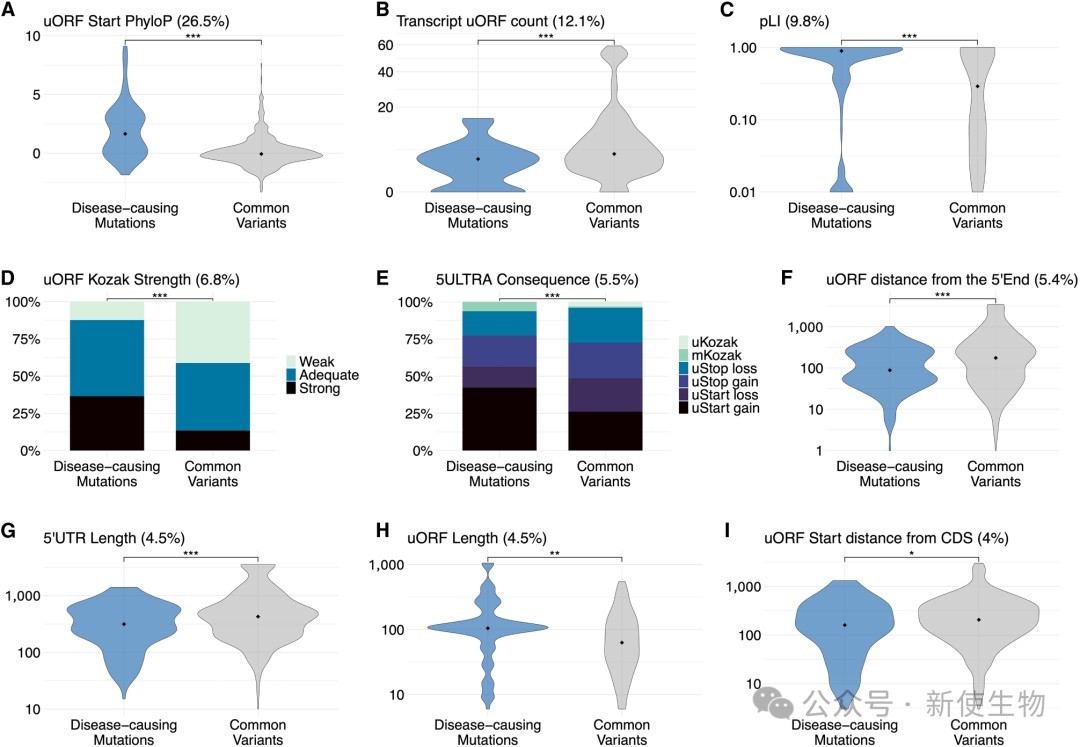
一、疾病相关基因倾向于规避uORF的翻译抑制
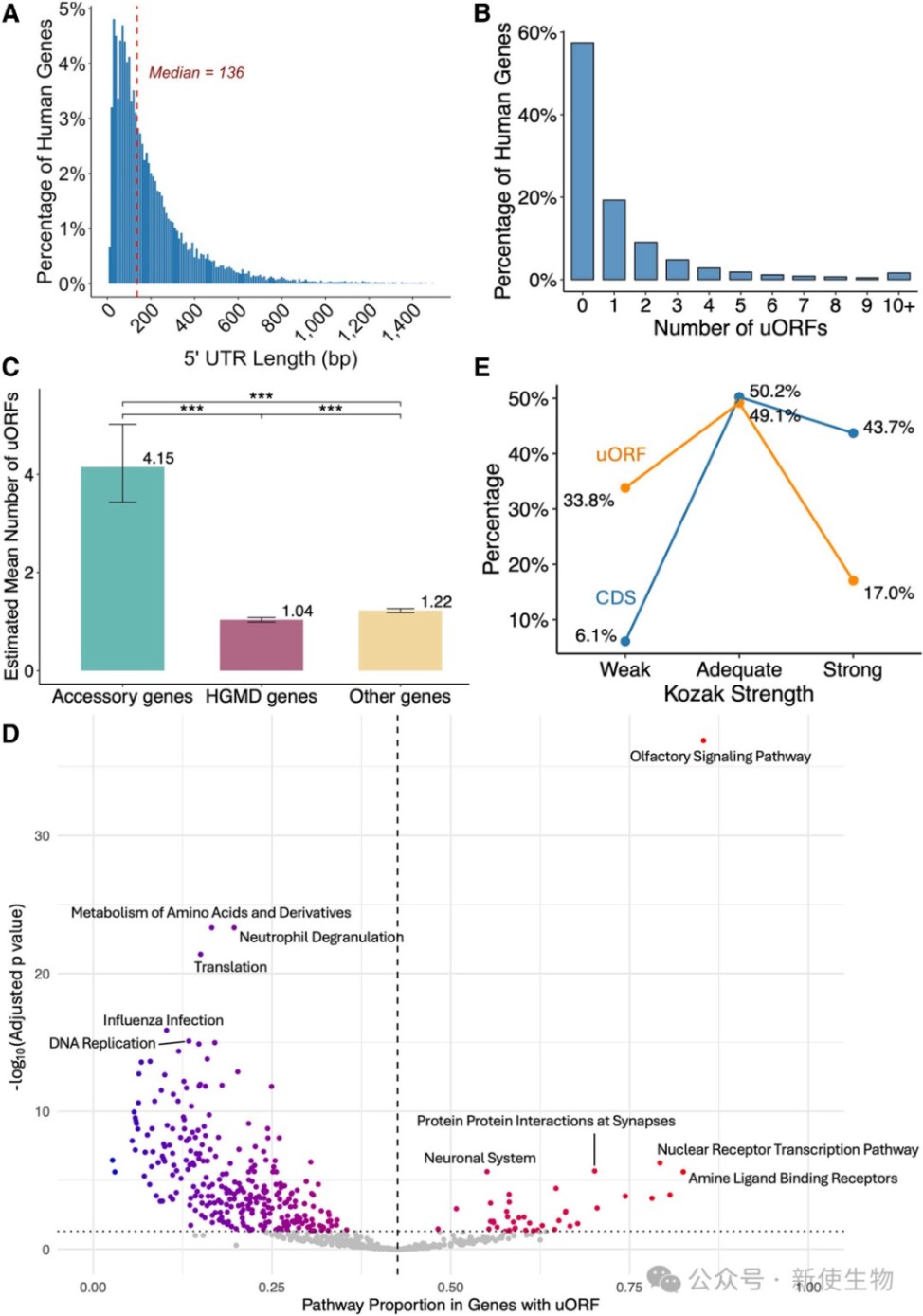
通过整合数据库并分析18775个转录本,发现42.5%的5' UTR含至少一个uORF,且其中35.7%的uORF具有Ribo-seq核糖体印迹分析支持的活跃翻译证据。
此外,致病基因中的uORF数量显著少于辅助功能基因,表明致病基因在维持翻译效率上受到更强的选择压力。
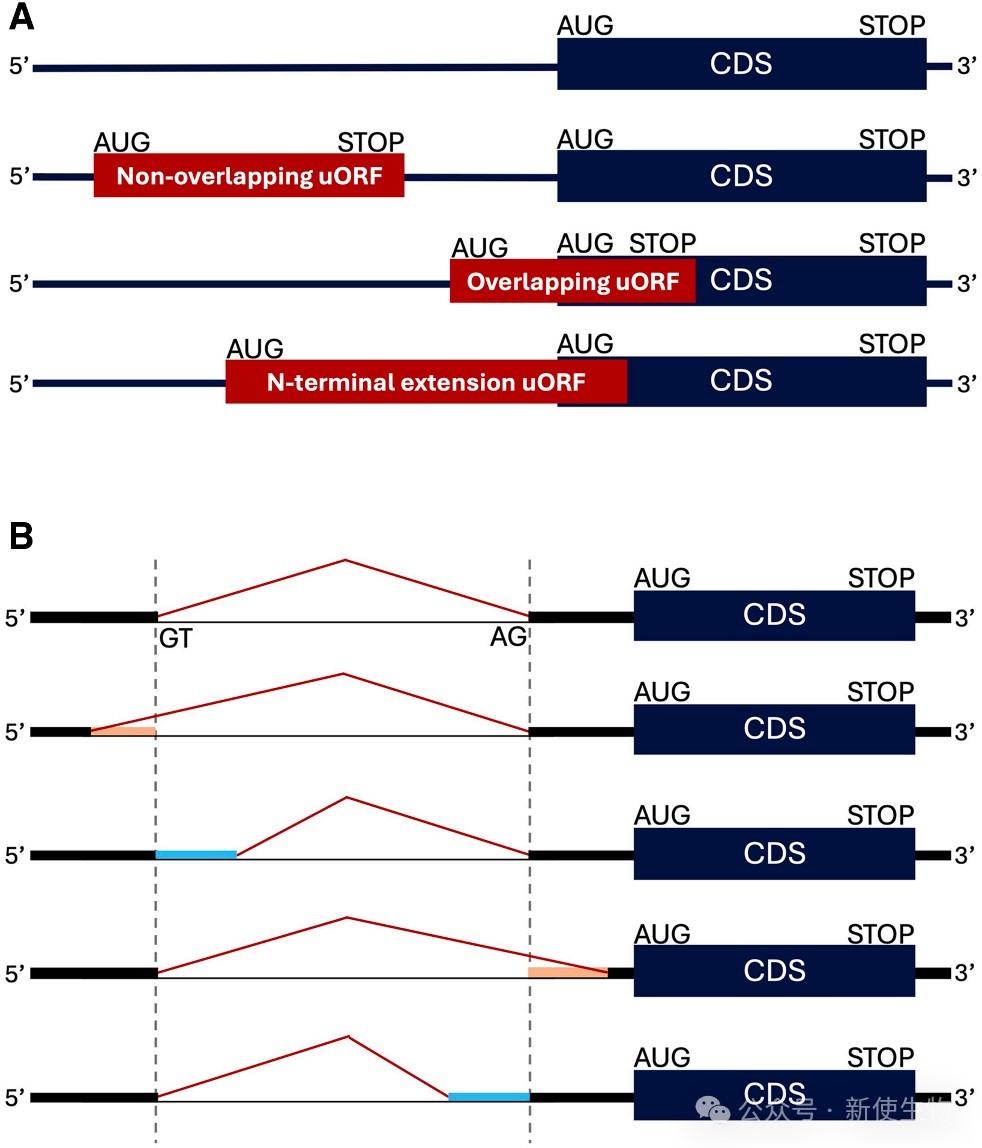
二、5ULTRA整合剪接预测以识别间接影响5' UTR的变异
该研究将SpliceAI算法整合进5ULTRA,使其能够识别位于外显子或内含子中但通过可变剪接来重塑5' UTR序列的变异。
这种方法扩展了变异检测范围,能够捕捉到间接影响uORF或Kozak序列的剪接变异。
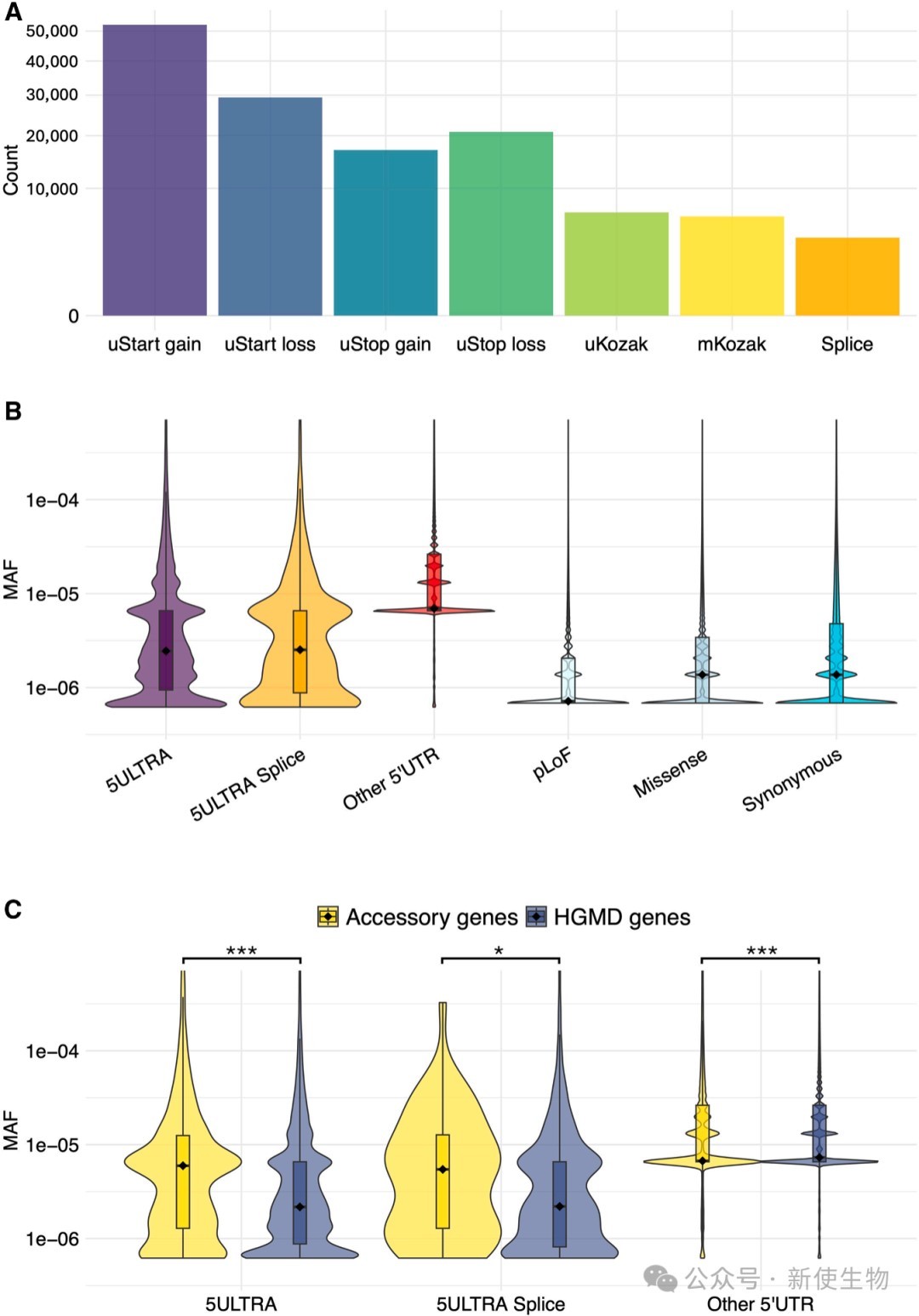
三、5ULTRA识别的变异在人群中更稀有且更保守
通过分析gnomAD数据库,发现经5ULTRA预测具有功能影响的变异,其等位基因频率(MAF)显著低于其他5' UTR变异,且其所在位点的物种间保守性更高。
四、5ULTRA评分能够高效、准确地优先排序致病性变异
研究团队基于HGMD致病变异和gnomAD常见变异训练了一个随机森林模型,生成了5ULTRA评分。
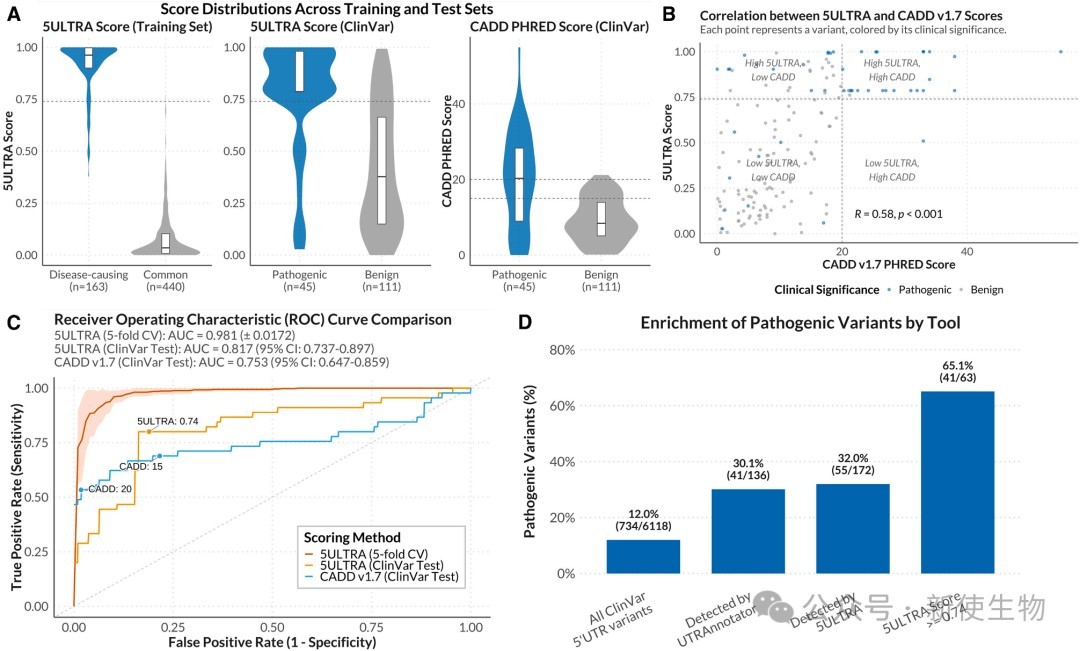
在独立的ClinVar测试集上,5ULTRA评分在区分致病与良性变异方面的表现优于通用预测工具CADD和专注uORF的UTRAnnotator,展示了更高的准确性和覆盖度。
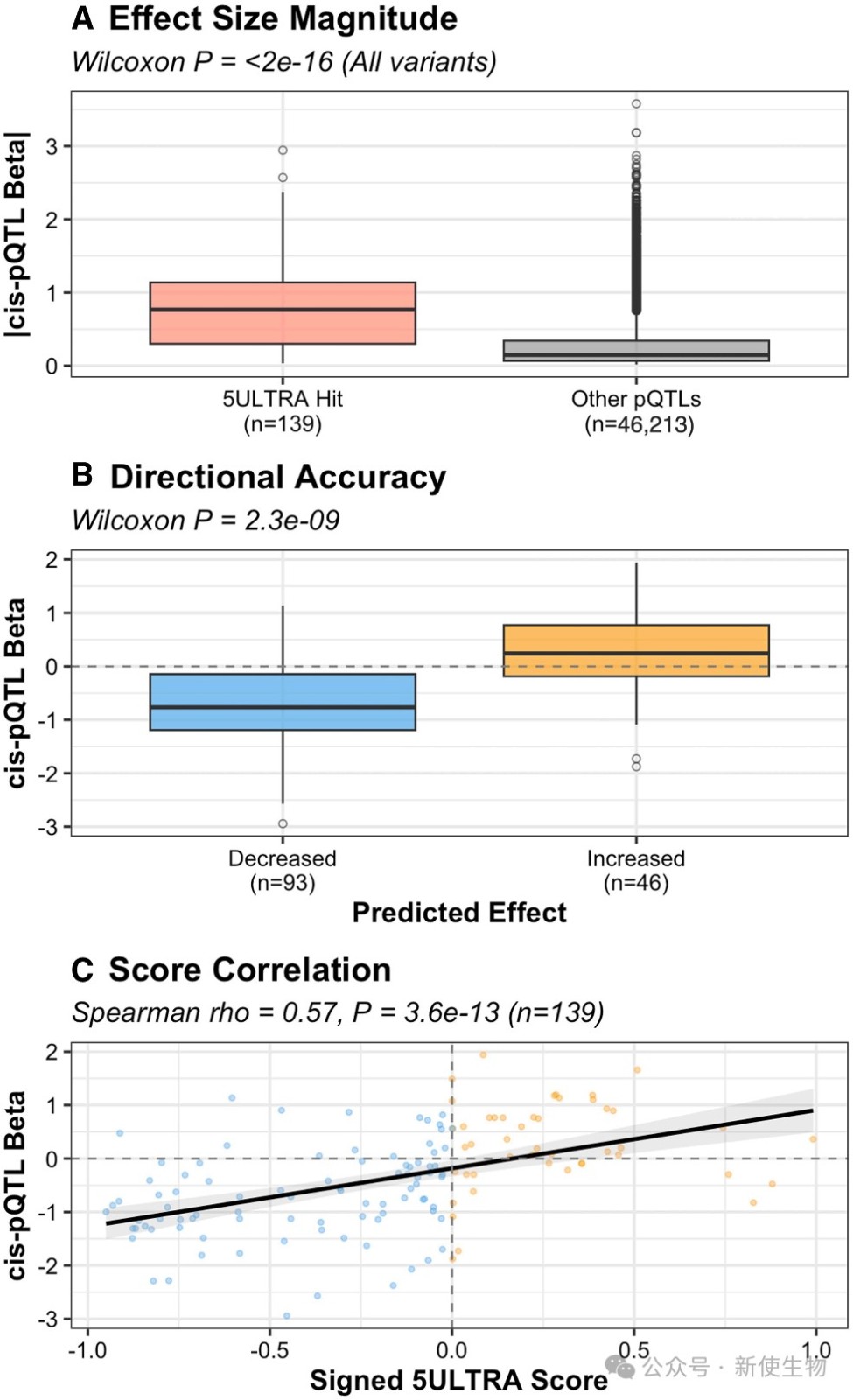
五、5ULTRA的预测与真实的蛋白质水平变化高度一致
将5ULTRA的预测结果与大规模蛋白质组学(pQTL)和高通量报告基因(MPRA)实验数据进行对比验证。
结果显示,5ULTRA识别的变异对蛋白质丰度的影响效应值显著更大,并且5ULTRA评分与实验测量的效应大小和方向均存在强相关性。
六、5ULTRA在多种疾病研究中成功鉴定出候选功能性变异
研究在COSMIC数据库中发现上千个潜在的癌症驱动变异,并解释了ABI1和NRAS变异如何通过改变翻译水平促进肿瘤。
同时,在临床队列中成功识别出导致先天性无脾症的RPSA剪接变异和增加结核病易感性的TNF变异,展示了该工具在临床诊断中的巨大潜力。
总结
本研究成功开发并验证了一个强大的计算工具5ULTRA,它能够系统性地识别并优先排序影响蛋白质翻译的人类5' UTR变异。通过在多种疾病背景下的应用,5ULTRA不仅揭示了5' UTR变异在人类遗传学中的重要作用,也为未来基因组学研究和精准医学提供了一个宝贵的资源。


 关于我们
关于我们 产品中心
产品中心 技术服务
技术服务 技术中心
技术中心 联系我们
联系我们